Supercomputer simuliert komplettes Virus in Aktion
Es dauerte nur einen winzigen Sekundenbruchteil, bedeutete jedoch einen biologisch-technischen Riesenschritt: Erstmals simulierten Forscher in den USA einen gesamten biologischen Organismus im Zusammenspiel seiner Moleküle in Aktion, und erhielten sogleich unerwartete Einblicke.
Urbana-Champaign (USA) - Die Simulation dauerte nur 50 Nanosekunden und es kam einer der größten Supercomputer der Welt zum Einsatz. Dies ist ein bedeutender Schritt für das Verständnis lebender Organismen. Bisher waren nur Simulationen von einzelnen Teilen von Viren gelungen, da der Rechenaufwand ungeheuer hoch ist. Ziel ist, eines Tages die Funktion komplizierter Viren im Modell nachzuvollziehen, sie besser zu verstehen als durch reine Beobachtung, oder sogar die komplexen Vorgänge in einer Zelle simulieren zu können. Möglich wäre dies nach Einschätzung der Forscher aber frühestens mit der nächsten Generation von Supercomputern in den kommenden fünf Jahren.
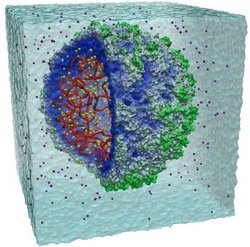
"Dieser Schritt wird die moderne Medizin unterstützen, während wir mehr darüber lernen, wie Viren leben", sagt Klaus Schulten, Physikprofessor an der University of Illinois Urbana-Champaign (UIUC). Beteiligt waren auch Kollegen in der Biophysik und Bioinformatik der Universität und Kristallographen der University of California in Irvine. Das Team wählte eine Variante des Tabakmosaikvirus, kugelförmig und so klein und einfach, dass es nur in Zellen gedeiht, die ein anderes Virus bereits befallen hat. Dennoch bestehen das Virus und der umgebende Wassertropfen, den die Forscher mit darstellten, aus zusammen mehr als einer Million Atomen. Ihre Interaktion auf einem heute üblichen PC zu simulieren, würde rund 35 Jahre dauern. Selbst den Supercomputer am National Center for Supercomputing Applications in Illinois brachte sie an seine Grenzen, selbst bei einer Simulation von milliardstel Sekunden Dauer, weil alle Atome gleichzeitig simuliert werden müssen. Die Modellrechnung gelang dank einer von Schultens Team entwickelter Software namens NAMD, entwickelt für die Simulation biologischer Moleküle, die Hunderte verschiedener Prozessoren eines Supercomputers zusammenschaltet, um gleichzeitig und gemeinsam das Problem zu berechnen.
Die Simulation brachte zwei überraschende Ergebnisse, berichten die Forscher im Fachblatt "Structure". Zum einen pulsiert das Virus offenbar asymmetrisch, als ob es atmen würde, obwohl es symmetrisch aufgebaut scheint. Zum anderen würde die Virushülle ohne die Erbgutmoleküle wohl zusammenklappen. Das lässt darauf schließen, dass das Virus bei seiner Vermehrung erst die Genstruktur und dann die Hülle darum herum baut, statt die RNA in die fertige Hülle zu bringen.
Wissenschaft aktuell
Quelle: https://www.weltderphysik.de/gebiet/leben/nachrichten/2006/supercomputer-simuliert-komplettes-virus-in-aktion/